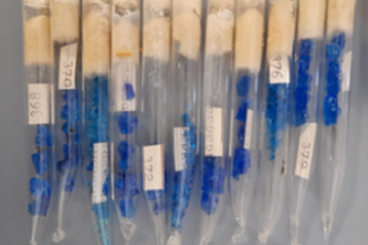
La disponibilità di un'ampia collezione di L. helveticus del 1970 presso il DISTAL ha fornito un quadro unico delle caratteristiche di questa specie e della sua diversità genetica.
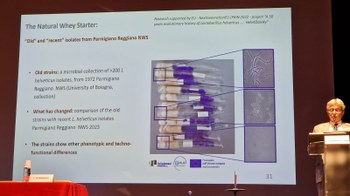
Il progetto Helv4DairHy è stato presentato all' 8th International Conference on Microbial Diversity (“Microbial Diversity for Empowering the Ecological Transition: Research, Innovation, and Technological Transfer”), svoltasi a Roma (23-26 settembre 2025).
Giulia Tabanelli e Alessia Levante hanno illustrato i progressi del progetto alla comunità scientifica internazionale. Nella sua Opening Lecture, il Prof. Neviani ha messo in evidenza il significato tecnologico degli ecosistemi microbici nelle nicchie lattiero-casearie con l’intervento “From single bacterial cells to microbial communities: the Natural Whey Starter.”

Questo studio rientra ha avuto lo scopo di investigare le dinamiche evolutive di Lactobacillus helveticus (LH) negli ambienti lattiero-caseari tradizionali negli ultimi cinquant’anni. Il lavoro si basa su due ampie collezioni di LH: una isolata e conservata nel 1970 da sieroinnesti naturali (NWS) impiegati per la produzione di formaggi DOP e mai rivitalizzata e depositata presso il DISTAL (UNIBO), e una seconda collezione isolata nel 2021–2023 dallo stesso contesto ecologico e tecnologico. La disponibilità di queste collezioni storiche e contemporanee ha offerto un’opportunità unica per confrontare la biodiversità di LH in un medesimo ambiente produttivo.
I ceppi sono stati inizialmente identificati e caratterizzati geneticamente mediante analisi AFLP, che ha evidenziato un’elevata biodiversità e una chiara differenziazione tra isolati storici e recenti. Sulla base di uno screening preliminare genotipico e fenotipico, sono stati selezionati 16 ceppi rappresentativi (comprendenti isolati sia vecchi che nuovi) per approfondimenti fisiologici, tecnologici e di sequenziamento genomico completo.
L’analisi genomica comparativa ha evidenziato cambiamenti evolutivi nel tempo, suggerendo un possibile fenomeno di riduzione genomica nei ceppi contemporanei. Dal punto di vista fenotipico, i ceppi storici hanno mostrato tassi di crescita più elevati e fasi lag più brevi in terreno colturale e in latte. Nei modelli caseari miniaturizzati che simulavano la produzione di formaggi a pasta cotta dura, sono emerse differenze nelle dinamiche microbiche e nella produzione di metaboliti: i ceppi storici tendevano a diminuire più rapidamente in concentrazione cellulare, probabilmente per fenomeni di lisi, accumulavano quantità inferiori di acido acetico e acetoino, ma producevano livelli più elevati di alcoli durante la maturazione.
Sulla base dei risultati genomici, fisiologici e tecnologici, quattro ceppi sono stati selezionati per prove di caseificazione su scala pilota: due storici e due recenti. I ceppi sono stati co-inoculati con un ceppo di Lactobacillus delbrueckii subsp. lactis UPCCO per riprodurre colture simili ai sieroinnesti naturali tradizionali. I formaggi sperimentali (~1 kg) sono stati prodotti in duplicato biologico utilizzando latte pastorizzato e un protocollo che simulava la produzione di formaggi a pasta dura cotta, con maturazione a 16 °C per tre settimane.
Le dinamiche microbiche sono state monitorate mediante conte microbiologiche e qPCR, mentre il profilo dei composti volatili è stato analizzato tramite SPME-GC-MS. I risultati hanno evidenziato differenze funzionali e metaboliche tra ceppi storici e recenti in termini di sviluppo microbico e produzione di composti volatili, fornendo nuove conoscenze sull’evoluzione microbica negli ecosistemi fermentativi lattiero-caseari e supportando la selezione mirata di ceppi per applicazioni casearie specifiche. Lo studio ha sottolineato la straordinaria importanza della conservazione della biodiversità microbica storica come risorsa biotecnologica per la selezione di nuovi ceppi di interesse industriale.